这里写目录标题
首先,简单提下Autodock vina 和 Autodock4的区别,可以这么理解,Autodock vina 是Autodock4的提升改进版本,vina拥有更好的计算方法和优化函数,分子对接速度和精确度会更高一些,如果是想要用分子对接进行一些实验验证,本文建议可以直接学习vina的软件操作,以下为vina的安装和环境配置流程。
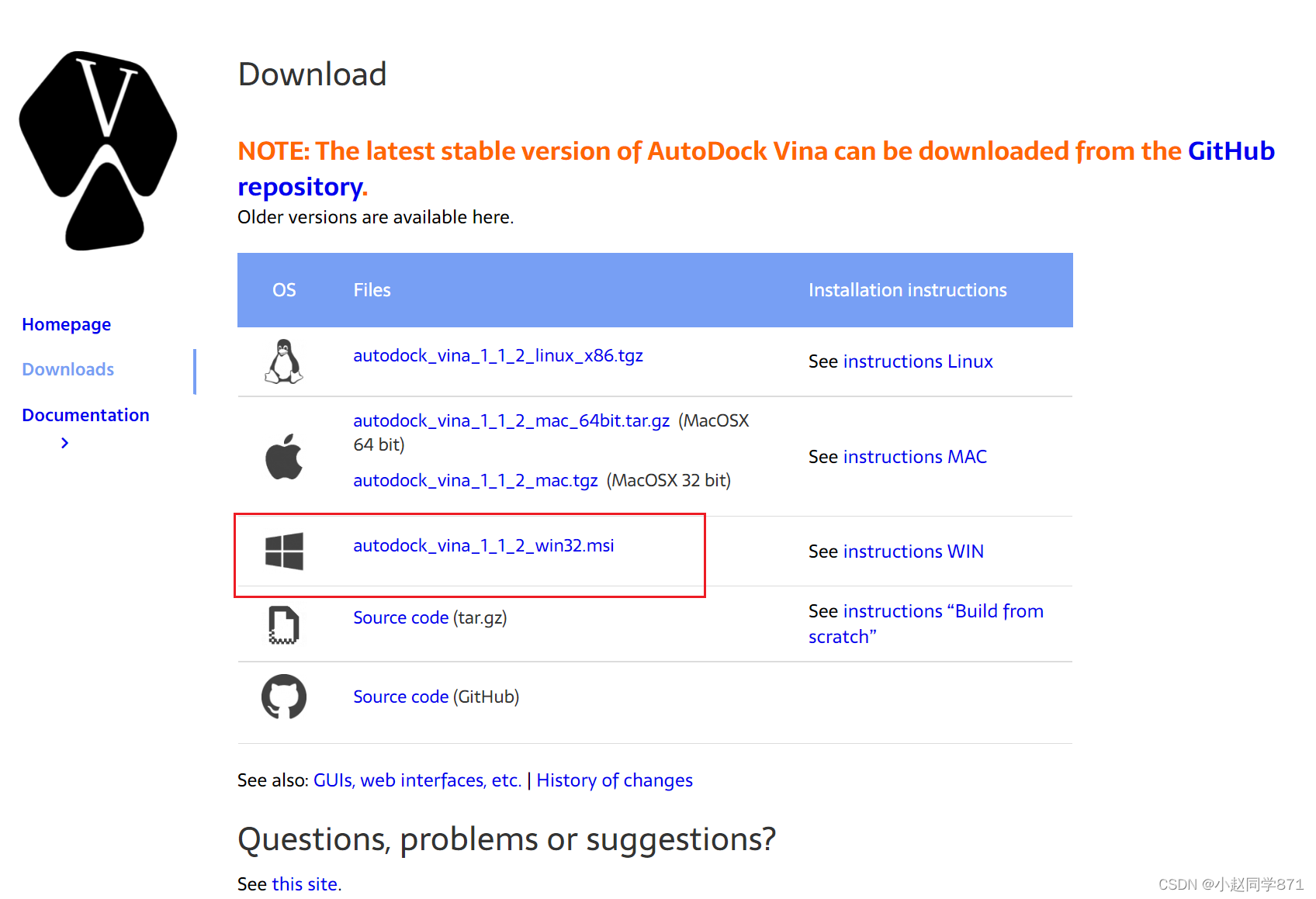
1.AutodockTools官网下载适合自己电脑的版本,这里windows系统只有32位的下载这个32位的即可
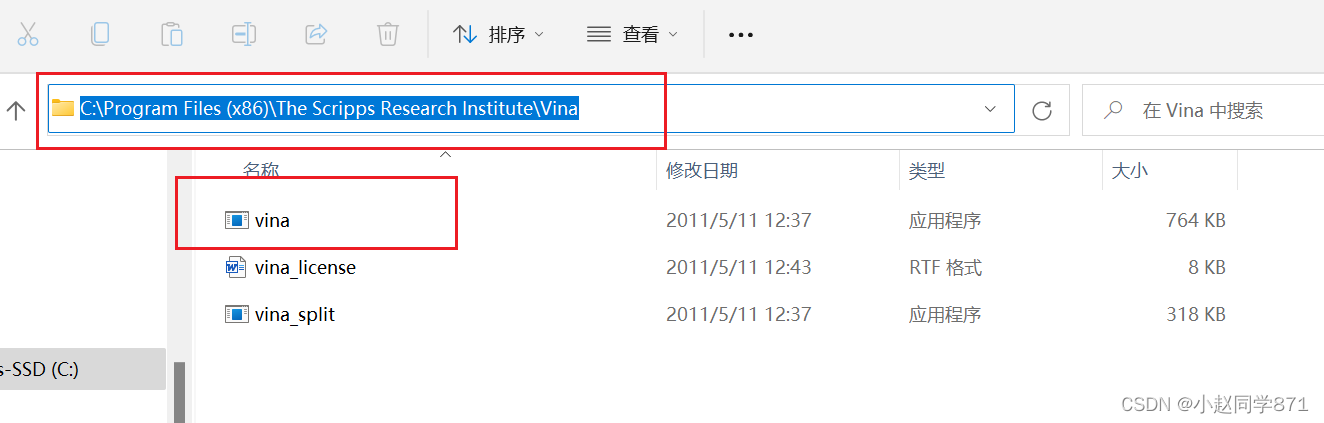
2.点击安装,默认安装即可,记住安装路径即可,安装好后找到这个路径文件夹里的adt文件下面圈起来的,
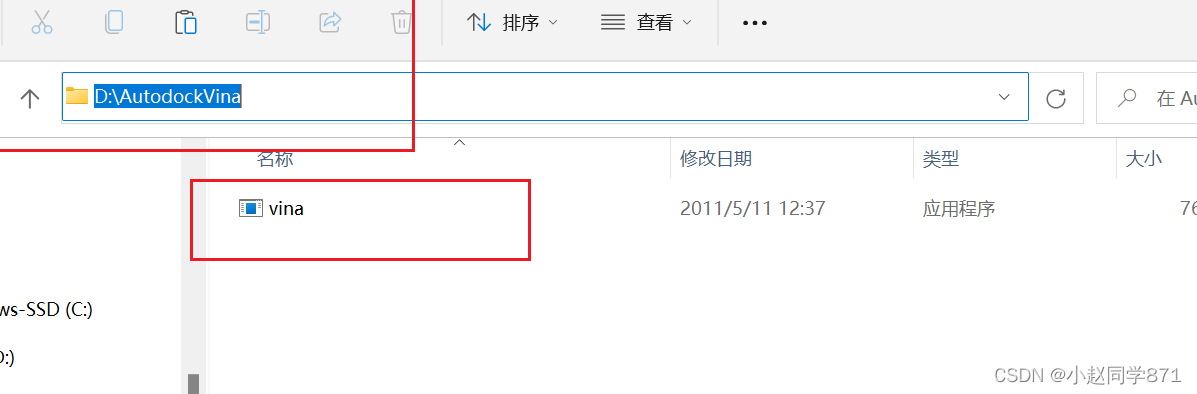
3.把adt复制到和上一步第4步vina.exe在一起的创建的默认文件夹中
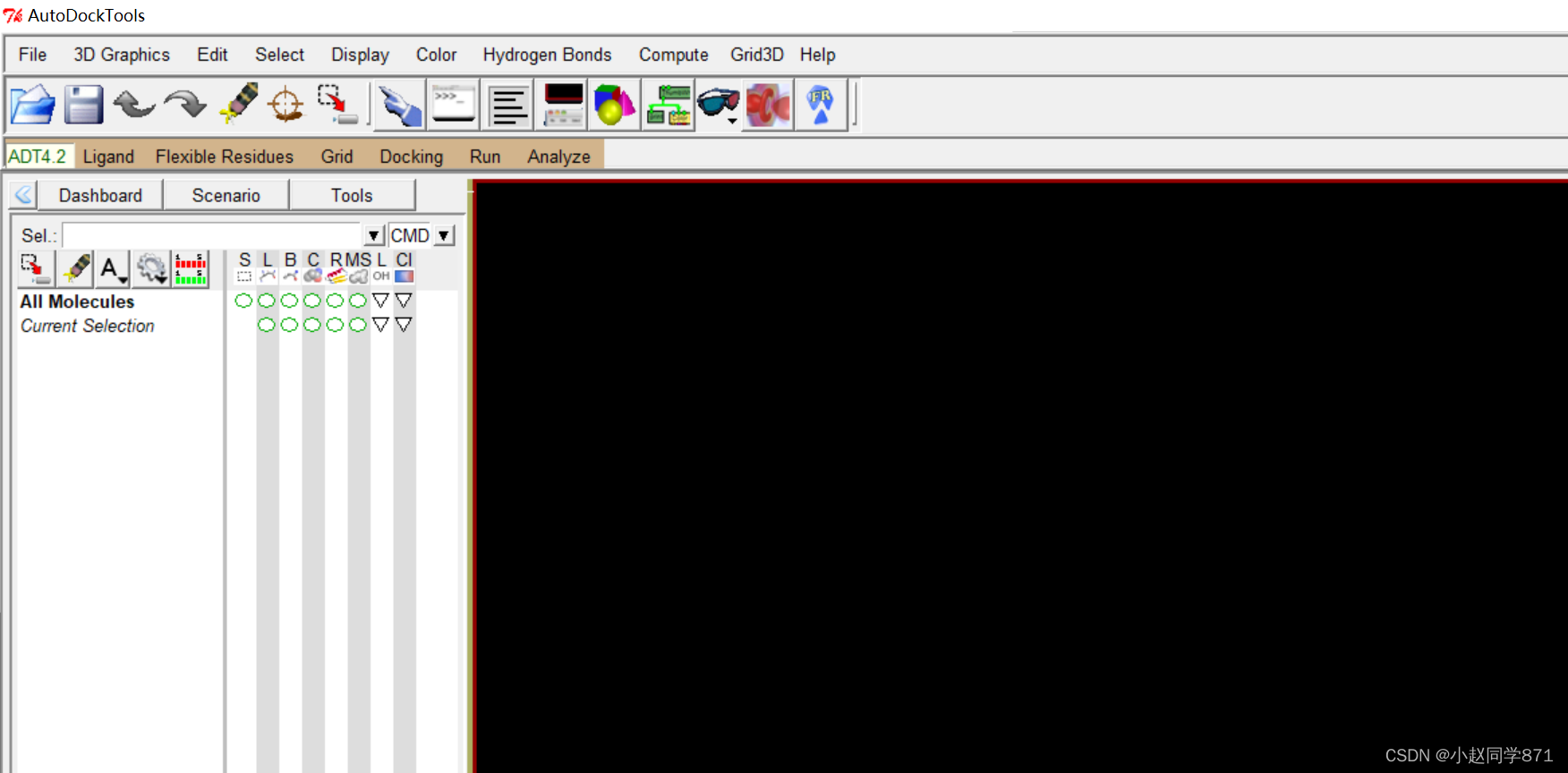
4.安装完成!点击adt即可打开AutoDockTools可视化界面,vina在这里也可以用。
先简单介绍下所要安装的其他版本,另外如果你觉得vina足够用,这步可以不用看
Autodock Vina :最近开发,不需要用户广泛的专业知识,经过高度优化,使用经过良好测试的默认方法执行对接实验,这个我们已经安装完全
QucikVina 2:对Autodock vina进行了不丢失准确率的提速
QucikVina – W:在QucikVina 2基础上增加了“Blind Docking”,比QuickVina2更快,并且比vina更准确
这三种vina的用法都是:
Vina –config config.txt
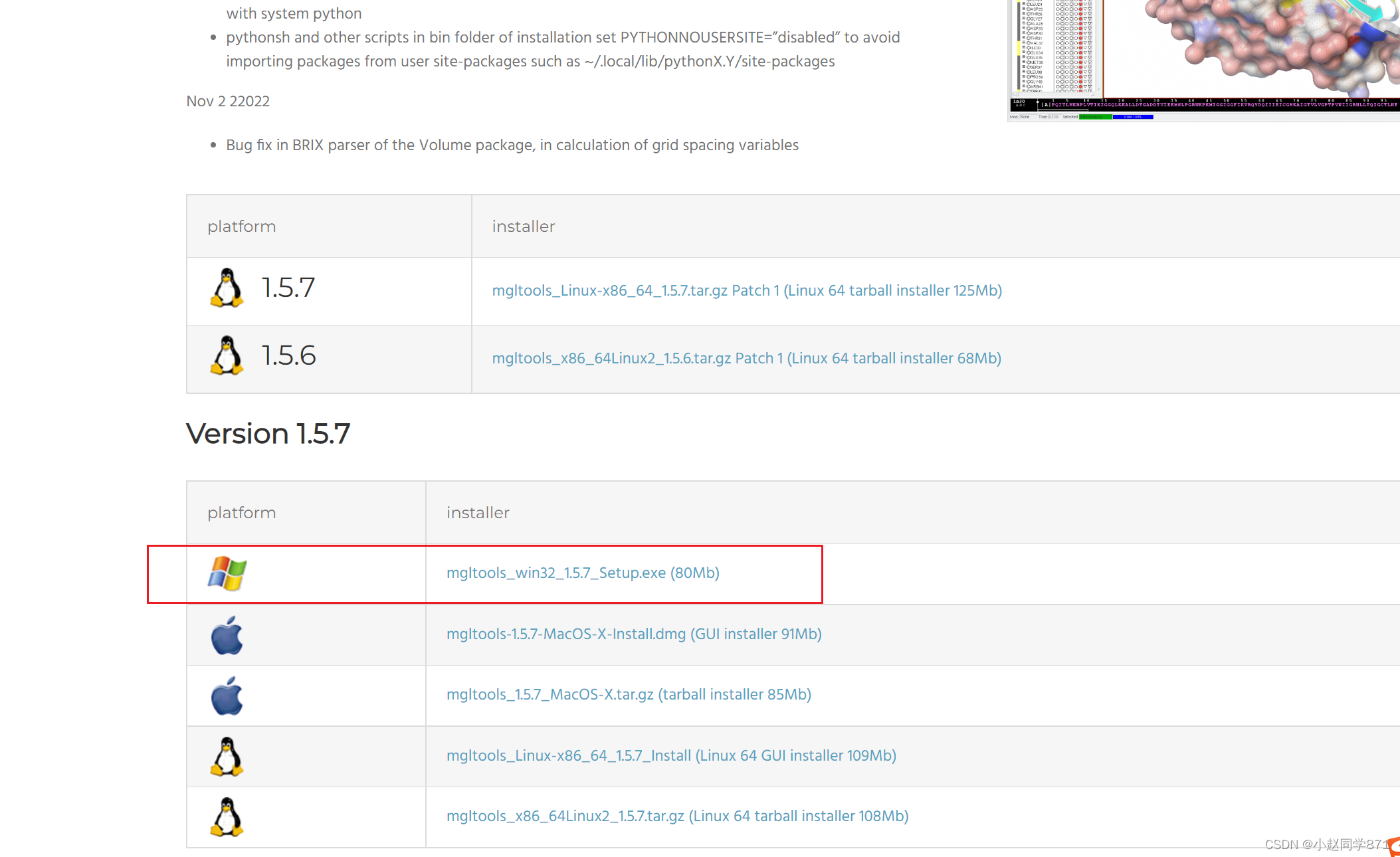
qvina官网,可以点进去了解下,qvina下载页面如下图我们点击下所圈的下载即可,由于是github可能网速比较慢,或者需要挂下梯子,和我们上面的adt和vina.exe文件放到一个盘里就行(实践证明放在哪里去终端都可以用,好强大!)下载这一个就行,qvina-2和qvina-w都可以用了,妙!
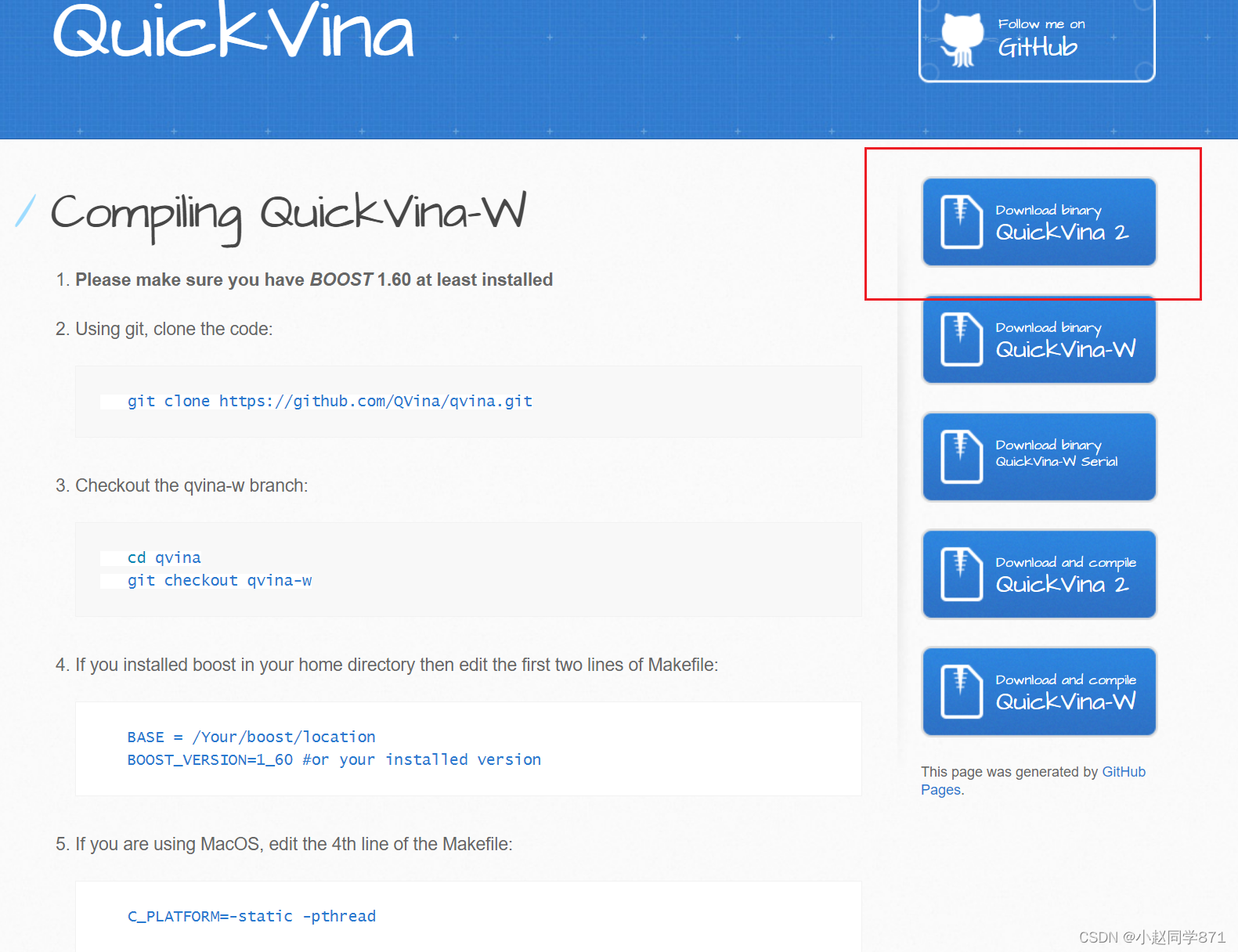
试验下是否可用
终端cmd输入,显示如下图即安装成功!
qvina
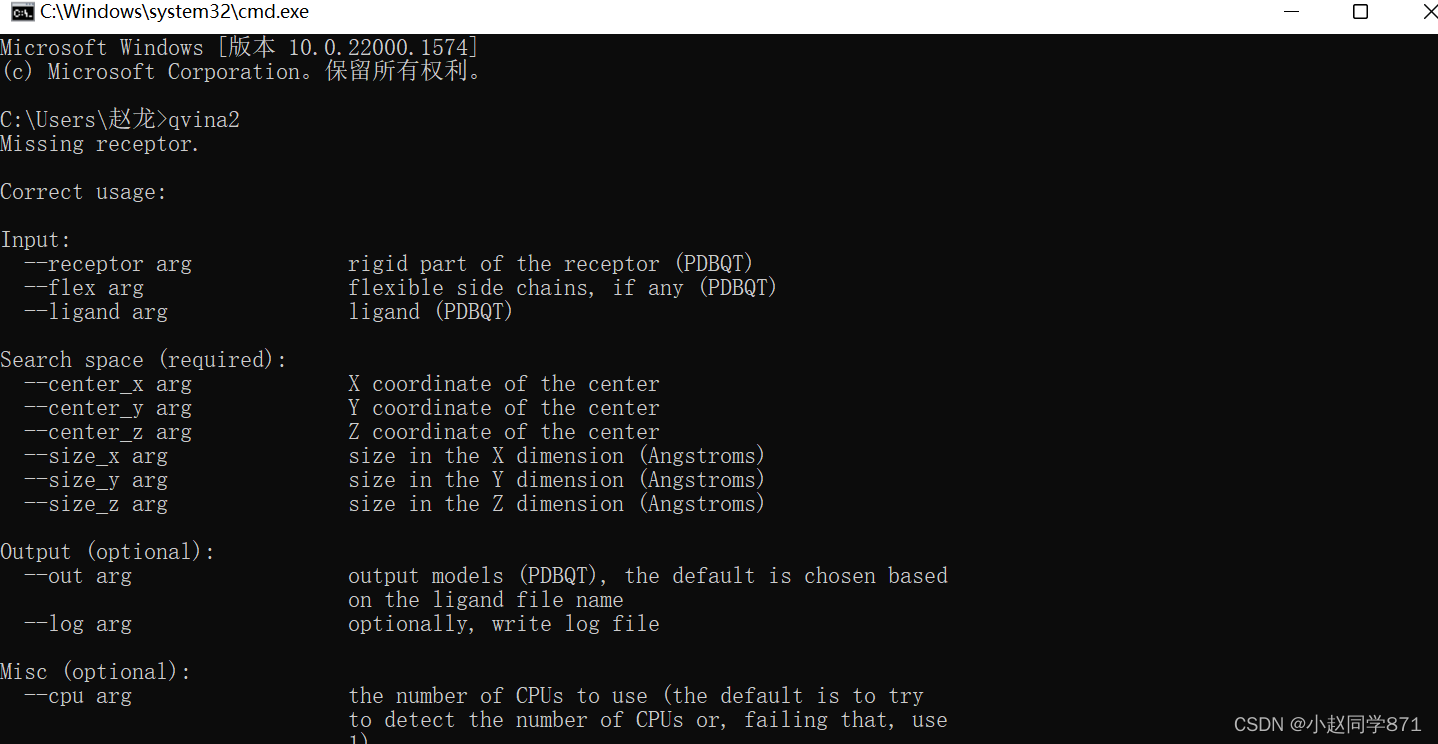
分子对接主要分为四个流程,如下图,各位学者且听我叙说:
1.受体获取
对于受体大分子首先我们要选择合适的受体大分子,即找到需要的受体大分子(蛋白质),常用的方法可以分为以下两种:
结构未知:同源建模构建受体三维结构;
结构已知:uniprot网站搜索同类蛋白,筛选所需蛋白,再通过PDB数据库下载。
对于结构已知的蛋白选择我们的筛选标准是选择X-ray射线晶体学测出来的蛋白质,选择分辨率尽量低的蛋白质,最好选择有配体分子复合物的共结晶结构。
2.受体处理
我们对蛋白质进行处理,所选用的工具是AutoDocktools和pymol,首先我们利用分子pymol对此复合物进行分离,将配体小分子去除,便于后面进行其他分子的对接。再利用AutoDocktools对此蛋白进行去水加氢,计算电荷,添加原子类型,具体操作如下:
受体需要去水、加全氢、导出为PDBQT(设置为受体)。具体操作如下:通过File→Read Molecular打开受体分子,然后分别对其进行去水(edit→delete water)、加极性氢(Edit→Hydrogens→Add→Polar Only→OK)、计算电荷(edit→Charges→Compute Gasteiger→确定)等操作,然后将蛋白分子选择为受体并保存受体为pdbqt格式(点击Grid→Macromolecule→Choose→选择受体→Select Molecule→确定→保存(默认路径))。
1.配体获取
1.TCMSP数据库
2.ZINC数据库
3.pubchem下载sdf格式,之后去Open Babel转化为mol2或pdb格式
4.在chemdraw上画出来,保存为sdf,再用Open babel转化
5.我们用网站(https://novopro.cn/tools/smiles2pdb.html)将smiles字符串直接转化为pdb格式。
2.配体处理
得到配体的pdb文件后我们将其用Autocktools打开进行调整电荷、选择配体可旋转的键的位置处理,具体操作如下:
配体预处理需要加氢、设置为配体(自动分布电荷)、检测扭转键、选择扭转键、导出为PDBQT等操作。具体如下:以同样的方式打开配体pdb文件,并加全氢(已加可不要此操作)、计算电荷,然后点击Ligand选项,点击Input→Choose→选择配体文件→确定,确定配体的可旋转键,操作为:点击Ligand,依次点击Torsion Tree→Detect Root;Torsion Tree→Choose Torsions→Done,点击ligand→Output→Save a PDBQT→保存。
Pdbqt是Autodock专用文件格式,方便处理。
1.确定结合位点
结合位点的特性:
1. 对接口袋通常呈现口袋状,如下图
2. 具有疏水性
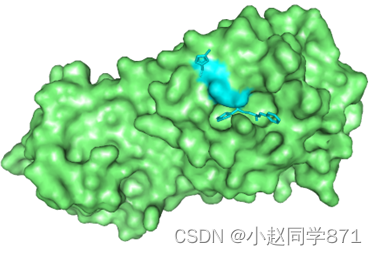
图活性口袋
确定结合位点的方法:
1. 文献/数据库调研法,
2. 实验筛查法:定点突变、荧光探针标记
3. 软件预测结合人工观察法
常用的软件预测有
https://playmolecule.com/deepsite/
https://proteins.plus/
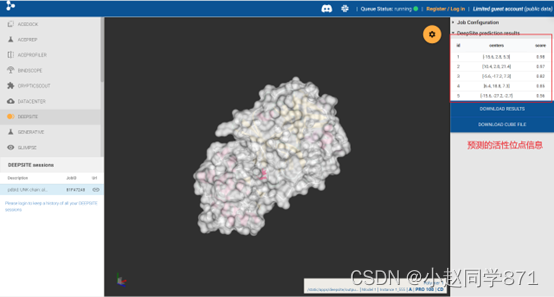
图deepsite
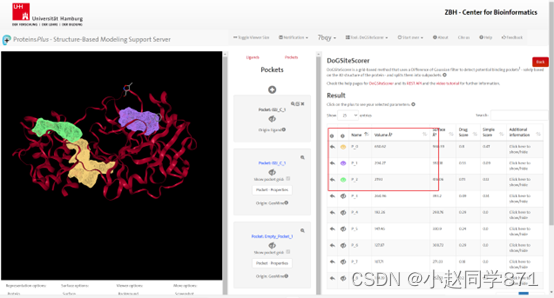
图Proteins.plus预测结合位点
4. 查看复合物共结晶结构的位置,配体的位置即活性位点位置,从AutoDock Tools中自行设置活性位点,如下图所示:
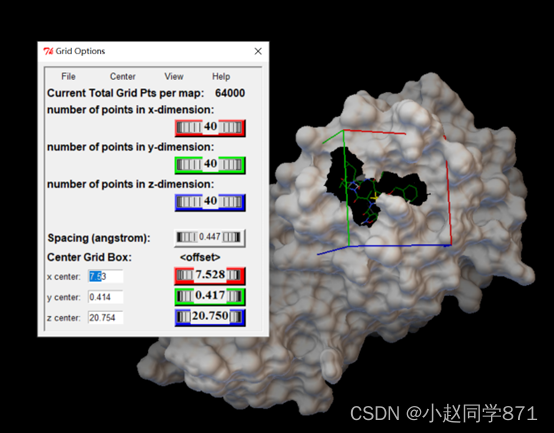
图根据配体位置确定活性位点
我们主要是采用第三种方法对接
2.设置对接盒子
利用AutoDockTools这个工具我们设置对接盒子,可以根据活性位点位置设置X,Y,Z坐标调整盒子大小完全包裹住活性口袋即可,对接盒子设置的越小运行越快,盒子越大运行越慢。记住这些盒子参数,方便后边使用。生成config.txt文件如下图
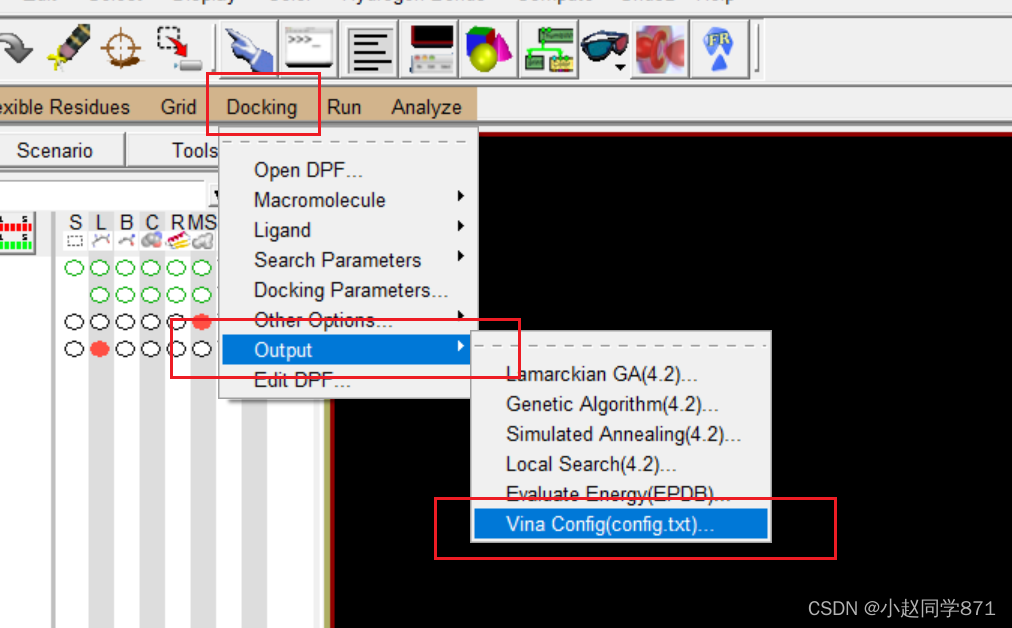
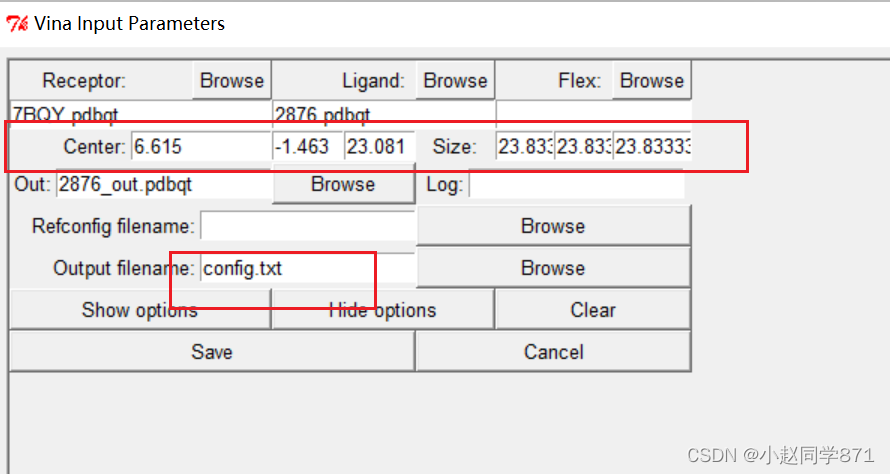
终端cmd(前提要打开AutoDockTools)然后输入以下指令
vina --config 自己生成的config文件

跑着如下图
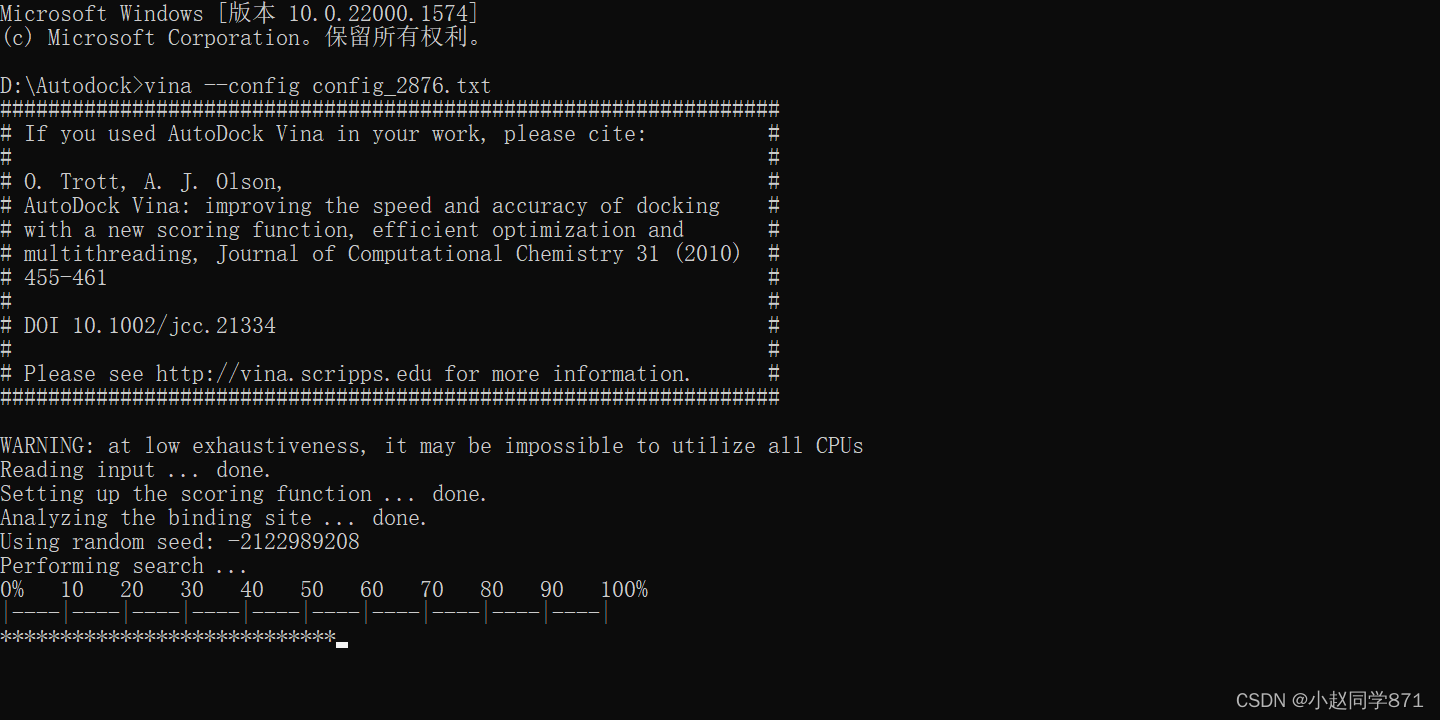
跑完如下图
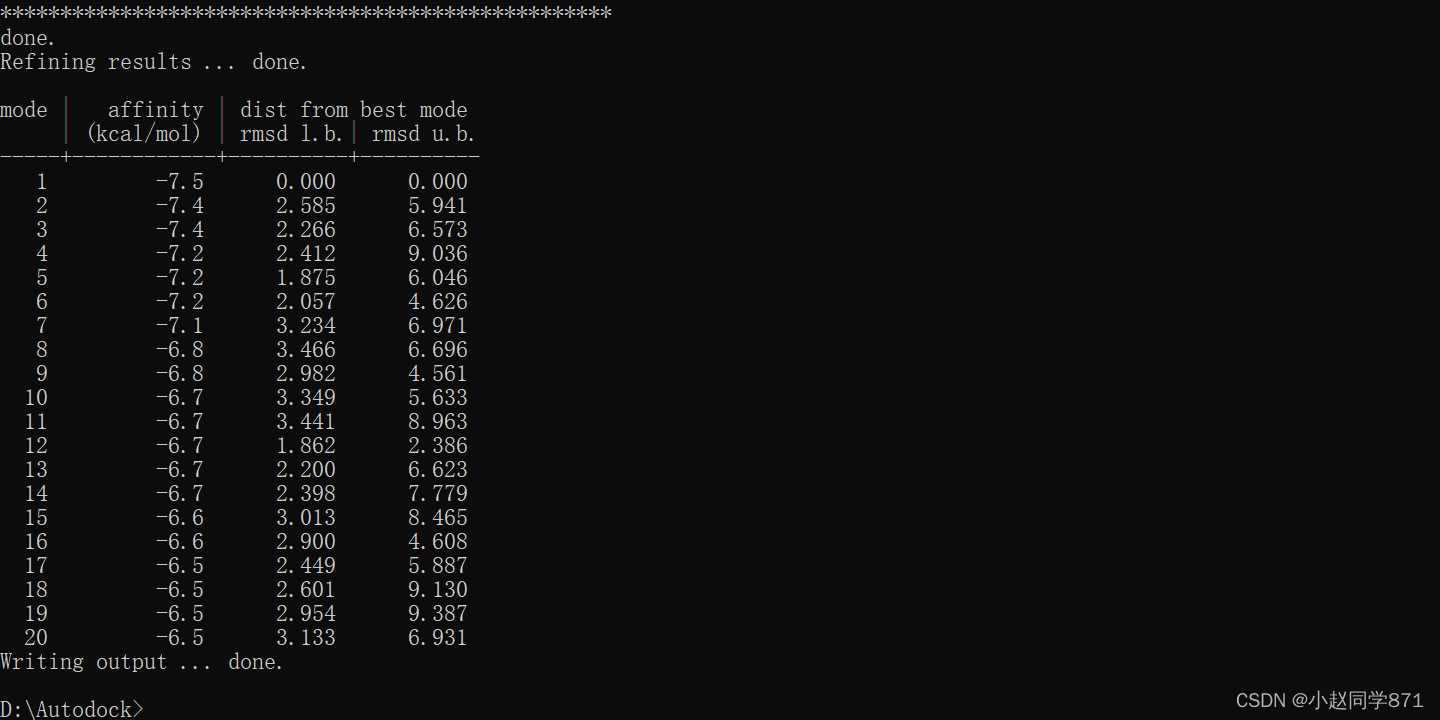
结果分析这块对于AutoDock4和vina都是适用的,可以套用。我们可以通过结合能、氢键两个角度对对接结果进行分析。
1.结合能分析
通过对接我们均可以得到配体和受体的结合能,我们挑选最低的结合能构象去进行结果分析。首先我们要清楚结合能的评判标准,对于Autodock系列的结合能评判标准为:通常情况下结合能越小,结合作用越好。结合能大于-4kcal/mol表明配体和受体结合作用较差,结合能在-4~-7kcal/mol表明配体和受体结合作用中等,结合能小于-7kcal/mol表明配体和受体之间结合能力较强。我们可以以此来分析所对接分子的效果。
2.氢键
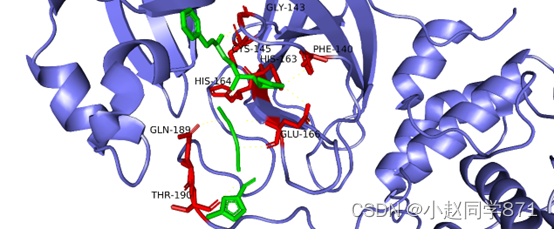
这块主要是生成一些更为直观地可视化图,去分析,观察是否与关键的氨基酸形成氢键作用,以此来证明我们所选配体分子的有效性。我们可以利用pymol生成如下图配体与受体复合物图。
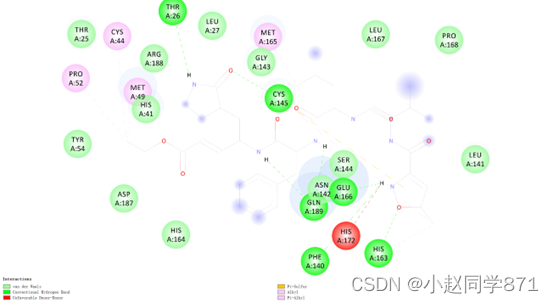
或者用Discovery studio生成如下图这种二维图
以上就是分子对接完整流程步骤,总结略显粗糙,大家海涵,互相学习交流,欢迎各位学者批评指正!
我想为Heroku构建一个Rails3应用程序。他们使用Postgres作为他们的数据库,所以我通过MacPorts安装了postgres9.0。现在我需要一个postgresgem并且共识是出于性能原因你想要pggem。但是我对我得到的错误感到非常困惑当我尝试在rvm下通过geminstall安装pg时。我已经非常明确地指定了所有postgres目录的位置可以找到但仍然无法完成安装:$envARCHFLAGS='-archx86_64'geminstallpg--\--with-pg-config=/opt/local/var/db/postgresql90/defaultdb/po
我打算为ruby脚本创建一个安装程序,但我希望能够确保机器安装了RVM。有没有一种方法可以完全离线安装RVM并且不引人注目(通过不引人注目,就像创建一个可以做所有事情的脚本而不是要求用户向他们的bash_profile或bashrc添加一些东西)我不是要脚本本身,只是一个关于如何走这条路的快速指针(如果可能的话)。我们还研究了这个很有帮助的问题:RVM-isthereawayforsimpleofflineinstall?但有点误导,因为答案只向我们展示了如何离线在RVM中安装ruby。我们需要能够离线安装RVM本身,并查看脚本https://raw.github.com/wayn
我有一个奇怪的问题:我在rvm上安装了rubyonrails。一切正常,我可以创建项目。但是在我输入“railsnew”时重新启动后,我有“程序'rails'当前未安装。”。SystemUbuntu12.04ruby-v"1.9.3p194"gemlistactionmailer(3.2.5)actionpack(3.2.5)activemodel(3.2.5)activerecord(3.2.5)activeresource(3.2.5)activesupport(3.2.5)arel(3.0.2)builder(3.0.0)bundler(1.1.4)coffee-rails(
我刚刚为fedora安装了emacs。我想用emacs编写ruby。为ruby提供代码提示、代码完成类型功能所需的工具、扩展是什么? 最佳答案 ruby-mode已经包含在Emacs23之后的版本中。不过,它也可以通过ELPA获得。您可能感兴趣的其他一些事情是集成RVM、feature-mode(Cucumber)、rspec-mode、ruby-electric、inf-ruby、rinari(用于Rails)等。这是我当前用于Ruby开发的Emacs配置:https://github.com/citizen428/emacs
我正在尝试在我的centos服务器上安装therubyracer,但遇到了麻烦。$geminstalltherubyracerBuildingnativeextensions.Thiscouldtakeawhile...ERROR:Errorinstallingtherubyracer:ERROR:Failedtobuildgemnativeextension./usr/local/rvm/rubies/ruby-1.9.3-p125/bin/rubyextconf.rbcheckingformain()in-lpthread...yescheckingforv8.h...no***e
我的最终目标是安装当前版本的RubyonRails。我在OSXMountainLion上运行。到目前为止,这是我的过程:已安装的RVM$\curl-Lhttps://get.rvm.io|bash-sstable检查已知(我假设已批准)安装$rvmlistknown我看到当前的稳定版本可用[ruby-]2.0.0[-p247]输入命令安装$rvminstall2.0.0-p247注意:我也试过这些安装命令$rvminstallruby-2.0.0-p247$rvminstallruby=2.0.0-p247我很快就无处可去了。结果:$rvminstall2.0.0-p247Search
我实际上是在尝试使用RVM在我的OSX10.7.5上更新ruby,并在输入以下命令后:rvminstallruby我得到了以下回复:Searchingforbinaryrubies,thismighttakesometime.Checkingrequirementsforosx.Installingrequirementsforosx.Updatingsystem.......Errorrunning'requirements_osx_brew_update_systemruby-2.0.0-p247',pleaseread/Users/username/.rvm/log/138121
由于fast-stemmer的问题,我很难安装我想要的任何rubygem。我把我得到的错误放在下面。Buildingnativeextensions.Thiscouldtakeawhile...ERROR:Errorinstallingfast-stemmer:ERROR:Failedtobuildgemnativeextension./System/Library/Frameworks/Ruby.framework/Versions/2.0/usr/bin/rubyextconf.rbcreatingMakefilemake"DESTDIR="cleanmake"DESTDIR=
这是一道面试题,我没有答对,但还是很好奇怎么解。你有N个人的大家庭,分别是1,2,3,...,N岁。你想给你的大家庭拍张照片。所有的家庭成员都排成一排。“我是家里的friend,建议家庭成员安排如下:”1岁的家庭成员坐在这一排的最左边。每两个坐在一起的家庭成员的年龄相差不得超过2岁。输入:整数N,1≤N≤55。输出:摄影师可以拍摄的照片数量。示例->输入:4,输出:4符合条件的数组:[1,2,3,4][1,2,4,3][1,3,2,4][1,3,4,2]另一个例子:输入:5输出:6符合条件的数组:[1,2,3,4,5][1,2,3,5,4][1,2,4,3,5][1,2,4,5,3][
当我尝试安装Ruby时遇到此错误。我试过查看this和this但无济于事➜~brewinstallrubyWarning:YouareusingOSX10.12.Wedonotprovidesupportforthispre-releaseversion.Youmayencounterbuildfailuresorotherbreakages.Pleasecreatepull-requestsinsteadoffilingissues.==>Installingdependenciesforruby:readline,libyaml,makedepend==>Installingrub