提示:基于前者代码的改进。原代码链接
根据前者提供的代码
在复现的过程中发现了一些改进的点(交叉和变异部分)
并且对每次迭代的结果进行了动态展示。
文章目录
代码运行可得到每一次迭代结果的图形,即为动态寻找最大值的过程。
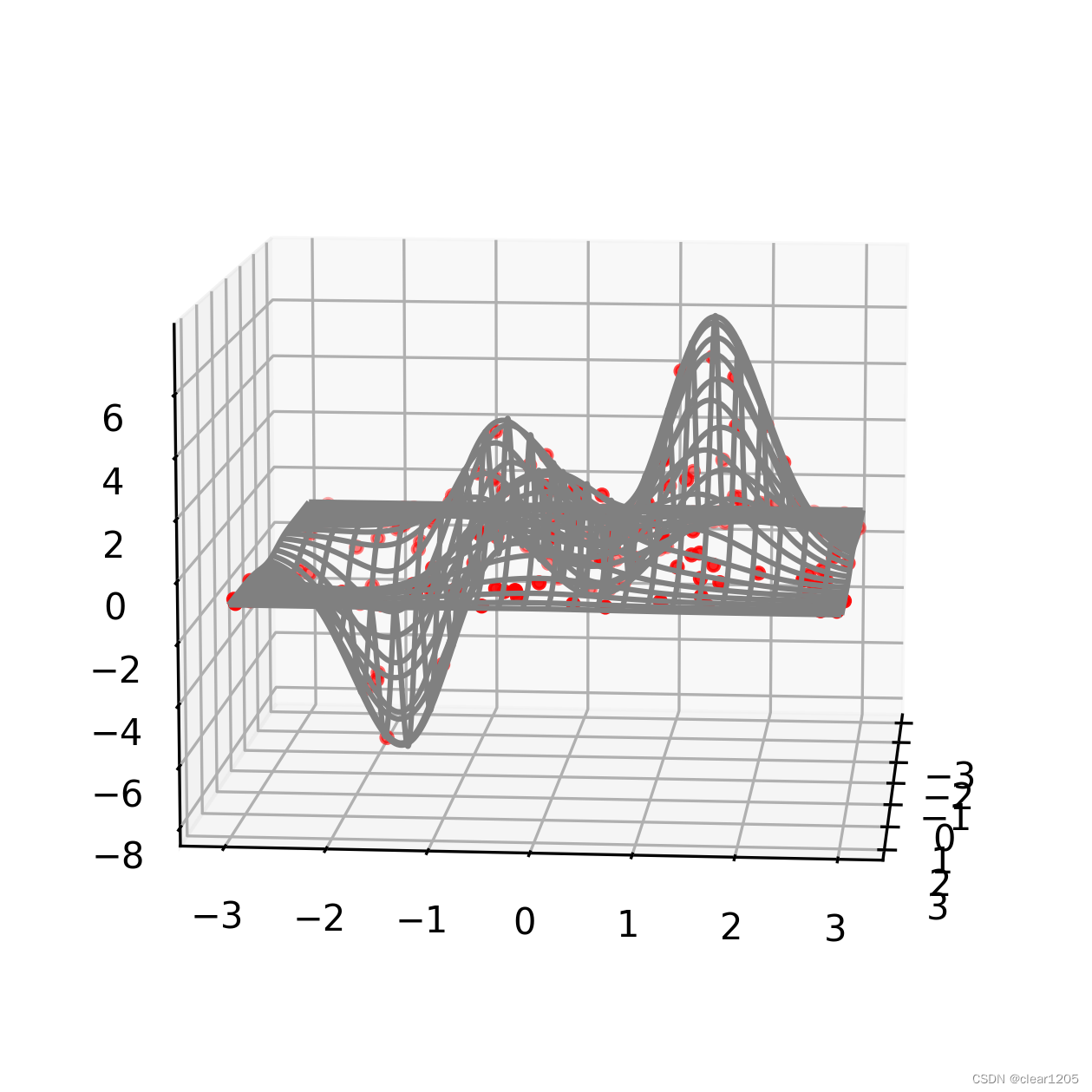
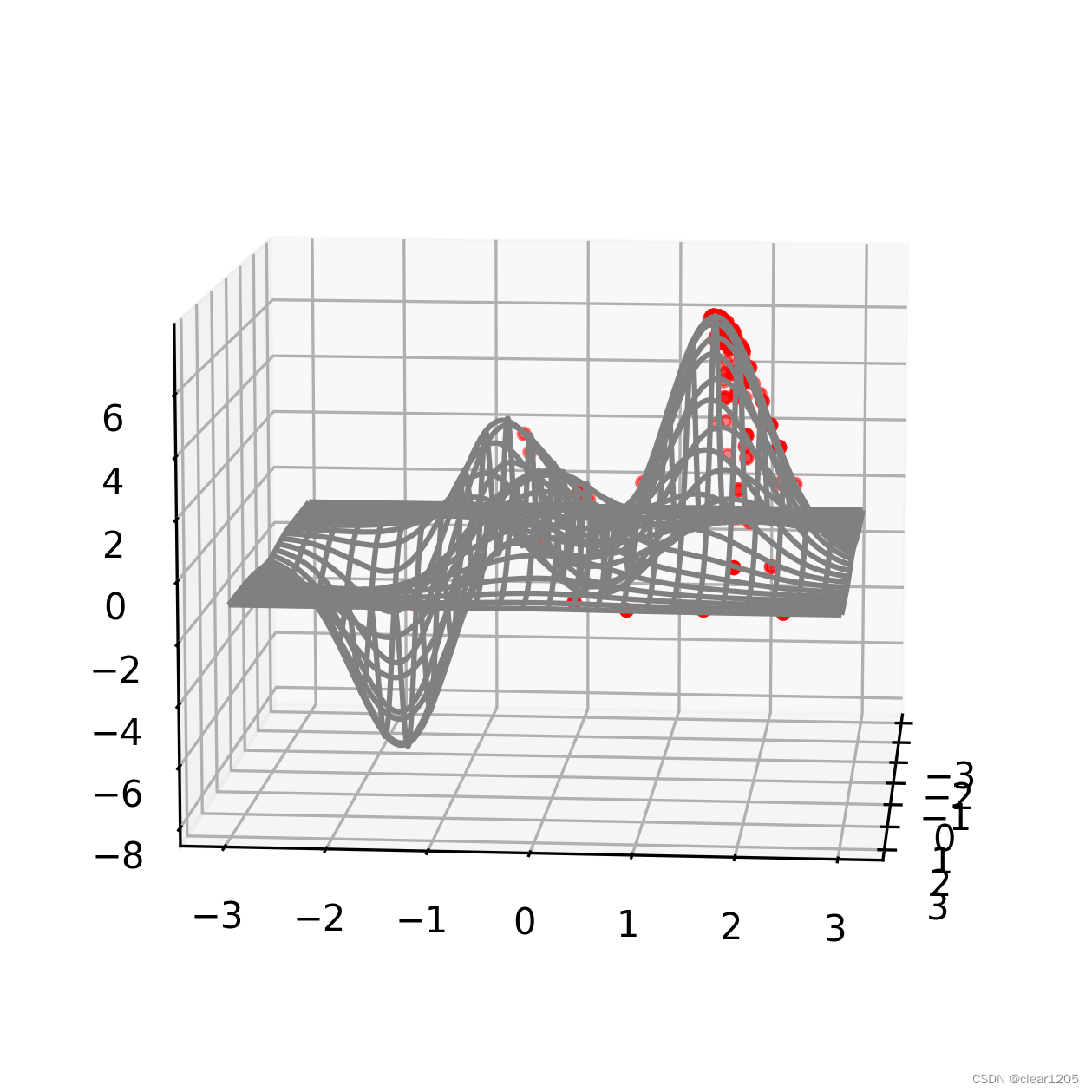
import numpy as np
import matplotlib.pyplot as plt
from mpl_toolkits.mplot3d import Axes3D
数值可以自行调整。
DNA_SIZE = 24
POP_SIZE = 200
CROSSOVER_RATE = 0.8
MUTATION_RATE = 0.02
N_GENERATIONS = 50
X_BOUND = [-3, 3]
Y_BOUND = [-3, 3]
定义函数F(x, y)
def F(x, y):
return 3*(1-x)**2*np.exp(-(x**2)-(y+1)**2) - 10*(x/5 - x**3 - y**5)*np.exp(-x**2-y**2) - 1/3**np.exp(-(x+1)**2 - y**2)
创建初始种群pop,POP_SIZE行DNA_SIZE*2列元素为0或1的二维矩阵。
pop = np.random.randint(0, 2, size=(POP_SIZE, DNA_SIZE*2))
构建网格坐标矩阵,画3D展示图是需要用,一维元组需要展开成二维矩阵。
X = np.linspace(X_BOUND[0], X_BOUND[1], 250)
Y = np.linspace(Y_BOUND[0], Y_BOUND[1], 250)
X, Y = np.meshgrid(X, Y)
Z = F(X, Y)
最后生成的三维点坐标即为(X, Y, Z)
函数np.meshgrid(X, Y)的详细说明和用法可参照这篇文章。
import numpy as np
import matplotlib.pyplot as plt
from mpl_toolkits.mplot3d import Axes3D
DNA_SIZE = 20
POP_SIZE = 200
CROSSOVER_RATE = 0.8
MUTATION_RATE = 0.05
N_GENERATIONS = 100
X_BOUND = [-3, 3]
Y_BOUND = [-3, 3]
def F(x, y):
return 3*(1-x)**2*np.exp(-(x**2)-(y+1)**2) - 10*(x/5 - x**3 - y**5)*np.exp(-x**2-y**2) - 1/3**np.exp(-(x+1)**2 - y**2)
X = np.linspace(X_BOUND[0], X_BOUND[1], 250)
Y = np.linspace(Y_BOUND[0], Y_BOUND[1], 250)
# 生成网格点坐标矩阵
X, Y = np.meshgrid(X, Y)
# 将网格矩阵坐标带入方程,求出方程的值。
Z = F(X, Y)
# 构建3维网格点坐标(X, Y, Z) X是行坐标矩阵,Y是列坐标矩阵,Z是高坐标矩阵。
# 将二进制的DNA转换成实数值,再求解函数值(适应度值)
def translateDNA(pop):
x_pop = pop[:, 1::2] # 奇数列表示X
y_pop = pop[:, ::2] # 偶数列表示y
# 矩阵A.dot(矩阵B) 矩阵A点乘矩阵B
# 将x y 对应到定义的区间内
trans_x = x_pop.dot(2**np.arange(DNA_SIZE)[::-1]) / \ float(2**DNA_SIZE-1)*(X_BOUND[1]-X_BOUND[0])+X_BOUND[0]
trans_y = y_pop.dot(2**np.arange(DNA_SIZE)[::-1]) / \ float(2**DNA_SIZE-1)*(Y_BOUND[1]-Y_BOUND[0])+Y_BOUND[0]
return trans_x, trans_y
# 求解种群中每一个个体的适应度
def get_fitness(pop):
x, y = translateDNA(pop)
pred = F(x, y)
return (pred - np.min(pred)) + 1e-3
# 将适应度的值>0
def select(pop, fitness): # nature selection wrt pop's fitness
pop_index = np.random.choice(np.arange(POP_SIZE), size=POP_SIZE, replace=True, p=(fitness)/(fitness.sum()))
return pop[pop_index]
# 原作者是随机确定一点,从这点到最后一段即为交叉的DNA片段,
# 但每次最后一段DNA都会进行交叉,丧失了部分随机性。莫烦Python的处理很高超,
# 使用了布尔值找出随机点的位置对DNA进行交叉操作,但每次都有一半的DNA片段进行交叉操作。
# 笔者的思路是对DNA进行剪接,找到两处随机点位置,对中间的片段进行交叉操作。
def crossover(pop):
cro_pop_index = []
for cro_index, father in zip(range(POP_SIZE), pop): # 遍历种群中的每一个个体,将该个体作为父亲
child = father # 孩子先得到父亲的全部基因
# 判断是否对这个个体进行交叉操作
if np.random.rand() < CROSSOVER_RATE: # 产生子代时不是必然发生交叉,而是以一定的概率发生交叉
mother = pop[np.random.randint(POP_SIZE)] # 在种群中选择另一个个体,并将该个体作为母亲
cross_point1 = np.random.randint(low=0, high=DNA_SIZE*2) # 随机产生的交叉点1
cross_point2 = np.random.randint(low=0, high=DNA_SIZE*2) # 随机产生的交叉点2
cross_start = min(cross_point1, cross_point2)
cross_end = max(cross_point1, cross_point2)
child[cross_start:cross_end] = mother[cross_start:cross_end]
# 记录进行交叉操作的个体位置
cro_pop_index.append(cro_index)
pop[cro_index] = child
return pop, cro_pop_index
def mutation(child):
for point_mut in range(DNA_SIZE*2):
if np.random.rand() < MUTATION_RATE: # 以MUTATION_RATE的概率进行变异
# 方案1
child[point_mut] = 1 if child[point_mut] == 0 else 0
# 方案2
# child[point_mut] = child[point_mut] ^ 1
# 将变异点的二进制为反转 child[] ^ 1 0变 1,1变 0。
return child
# plt.ico() plt.ioff()将画图模式改为交互模式,程序遇到plt.show不会暂停,而是继续执行
plt.ion()
# 设定初始sca对象,以免报错;无实际作用
sca = plt.scatter(1, 1)
# 构建初始解
pop = np.random.randint(0, 2, size=(POP_SIZE, DNA_SIZE*2))
# 遗传算法迭代N代
for N in range(N_GENERATIONS):
x, y = translateDNA(pop)
# 画图展示每一次结果
if 'sca' in globals():
sca.remove()
fig = plt.figure(dpi=300)
# sca = ax.scatter(x, y, F(x, y), c='red', marker='o', s=15)
ax = Axes3D(fig)
sca = ax.scatter(x, y, F(x, y), c='red', marker='o', s=10)
# ax2=ax1.twin()
ax.plot_wireframe(X, Y, Z, rstride=10, cstride=10, color='gray')
# plt.gca().view_init(elev, azim) 设置网格线密度
plt.gca().view_init(10, 5)
plt.show()
plt.pause(0.01)
pop, cro_pop_index = crossover(pop) # 交叉
for mut_index in cro_pop_index: # 变异
child = pop[mut_index]
child = mutation(child)
pop[mut_index] = child
fitness = get_fitness(pop)
pop = select(pop, fitness) # 选择生成新的种群
plt.ioff()
max_fitness_index = np.argmax(fitness)
# print("max_fitness:", fitness[max_fitness_index])
print("最优的基因型:", pop[max_fitness_index])
print("x={:.2f}, y={:.2f}".format(x[max_fitness_index], y[max_fitness_index]))
print("F(x, y)= {:.3f}".format(F(x[max_fitness_index], y[max_fitness_index])))
test = str(F(x[max_fitness_index], y[max_fitness_index]))
with open(r'H:\遗传算法.txt', 'w') as f:
f.write(test)
我想在一个没有Sass引擎的类中使用Sass颜色函数。我已经在项目中使用了sassgem,所以我认为搭载会像以下一样简单:classRectangleincludeSass::Script::FunctionsdefcolorSass::Script::Color.new([0x82,0x39,0x06])enddefrender#hamlengineexecutedwithcontextofself#sothatwithintemlateicouldcall#%stop{offset:'0%',stop:{color:lighten(color)}}endend更新:参见上面的#re
我正在尝试用ruby中的gsub函数替换字符串中的某些单词,但有时效果很好,在某些情况下会出现此错误?这种格式有什么问题吗NoMethodError(undefinedmethod`gsub!'fornil:NilClass):模型.rbclassTest"replacethisID1",WAY=>"replacethisID2andID3",DELTA=>"replacethisID4"}end另一个模型.rbclassCheck 最佳答案 啊,我找到了!gsub!是一个非常奇怪的方法。首先,它替换了字符串,所以它实际上修改了
我有一些代码在几个不同的位置之一运行:作为具有调试输出的命令行工具,作为不接受任何输出的更大程序的一部分,以及在Rails环境中。有时我需要根据代码的位置对代码进行细微的更改,我意识到以下样式似乎可行:print"Testingnestedfunctionsdefined\n"CLI=trueifCLIdeftest_printprint"CommandLineVersion\n"endelsedeftest_printprint"ReleaseVersion\n"endendtest_print()这导致:TestingnestedfunctionsdefinedCommandLin
目录一.加解密算法数字签名对称加密DES(DataEncryptionStandard)3DES(TripleDES)AES(AdvancedEncryptionStandard)RSA加密法DSA(DigitalSignatureAlgorithm)ECC(EllipticCurvesCryptography)非对称加密签名与加密过程非对称加密的应用对称加密与非对称加密的结合二.数字证书图解一.加解密算法加密简单而言就是通过一种算法将明文信息转换成密文信息,信息的的接收方能够通过密钥对密文信息进行解密获得明文信息的过程。根据加解密的密钥是否相同,算法可以分为对称加密、非对称加密、对称加密和非
如何在Ruby中按名称传递函数?(我使用Ruby才几个小时,所以我还在想办法。)nums=[1,2,3,4]#Thisworks,butismoreverbosethanI'dlikenums.eachdo|i|putsiend#InJS,Icouldjustdosomethinglike:#nums.forEach(console.log)#InF#,itwouldbesomethinglike:#List.iternums(printf"%A")#InRuby,IwishIcoulddosomethinglike:nums.eachputs在Ruby中能不能做到类似的简洁?我可以只
说在前面这部分我本来是合为一篇来写的,因为目的是一样的,都是通过独立按键来控制LED闪灭本质上是起到开关的作用,即调用函数和中断函数。但是写一篇太累了,我还是决定分为两篇写,这篇是调用函数篇。在本篇中你主要看到这些东西!!!1.调用函数的方法(主要讲语法和格式)2.独立按键如何控制LED亮灭3.程序中的一些细节(软件消抖等)1.调用函数的方法思路还是比较清晰地,就是通过按下按键来控制LED闪灭,即每按下一次,LED取反一次。重要的是,把按键与LED联系在一起。我打算用K1来作为开关,看了一下开发板原理图,K1连接的是单片机的P31口,当按下K1时,P31是与GND相连的,也就是说,当我按下去时
我需要一个通过输入字符串进行计算的方法,像这样function="(a/b)*100"a=25b=50function.something>>50有什么方法吗? 最佳答案 您可以使用instance_eval:function="(a/b)*100"a=25.0b=50instance_evalfunction#=>50.0请注意,使用eval本质上是不安全的,尤其是当您使用外部输入时,因为它可能包含注入(inject)的恶意代码。另请注意,a设置为25.0而不是25,因为如果它是整数a/b将导致0(整数)。
我需要用任何语言编写一个算法,根据3个因素对数组进行排序。我以度假村为例(如Hipmunk)。假设我想去度假。我想要最便宜的地方、最好的评论和最多的景点。但是,显然我找不到在所有3个中都排名第一的方法。Example(assumingthereare20importantattractions):ResortA:$150/night...98/100infavorablereviews...18of20attractionsResortB:$99/night...85/100infavorablereviews...12of20attractionsResortC:$120/night
我需要从json记录中获取一些值并像下面这样提取curr_json_doc['title']['genre'].map{|s|s['name']}.join(',')但对于某些记录,curr_json_doc['title']['genre']可以为空。所以我想对map和join()使用try函数。我试过如下curr_json_doc['title']['genre'].try(:map,{|s|s['name']}).try(:join,(','))但是没用。 最佳答案 你没有正确传递block。block被传递给参数括号外的方法
我正在处理http://prepwork.appacademy.io/mini-curriculum/array/中概述的数组问题我正在尝试创建函数my_transpose,它接受一个矩阵并返回其转置。我对写入二维数组感到很困惑!这是一个代码片段,突出了我的困惑。rows=[[0,1,2],[3,4,5],[6,7,8]]columns=Array.new(3,Array.new(3))putscolumns.to_s#Outputisa3x3arrayfilledwithnilcolumns[0][0]=0putscolumns.to_s#Outputis[[0,nil,nil],[